简介
该用户还未填写简介
擅长的技术栈
可提供的服务
暂无可提供的服务
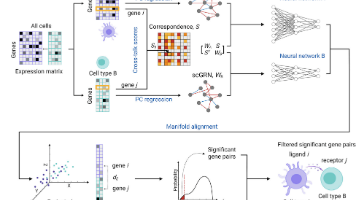
最近的一个热点那肯定是 bulk 与单细胞的联合分析,不过肯定不是差异+单细胞注释分群,而是直接意义上的通过算法建模两种数据。除了 ATAC 数据以外,作者也在黑色素瘤的单细胞转录组的数据中进行了示例分析,可以看到与其它方法相比更加联系的疾病关联细胞鉴定。在此基础上,根据下面的流程构建 bulk 样本与每个单细胞之间的相似性矩阵,再衡量每个细胞与目标表型之间的关联强度,最后将候选细胞与表型一起构建
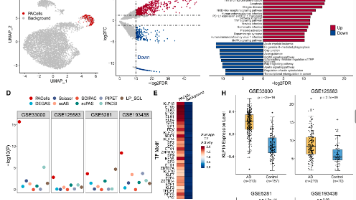
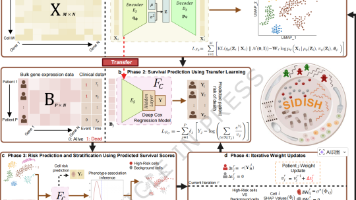
④ 第四阶段用 SHAP 量化基因对 High-Risk 判别的贡献,并把贡献映射回 W,同时将患者风险更新回 v,让单细胞与bulk的信号在循环中迭代更新(有种EM算法的感觉了,这种神经网络的EM这几年其实还不少)。尽管紫色也有,但是没有蓝色的多。该框架以迭代反馈的方式,把 bulk 队列中的预后信息整合到单细胞表示学习中,从而识别与预后不良结局相关的 High-Risk 细胞群,并在此基础上进
生信碱移TCMNP 包,一路打通网络药理学数据库与可视化分析。最近,小编冲浪的时候看到一个今年发表的网络药理学 R 包 TCMNP,据说整合了多个数据库以及多种可视化分析函数,一眼看下来确实够顶。具体来说,TCMNP 整合了几大类型的数据库:① 三大药物成分及靶点数据库TCMSP、DrugBank、ETCM;② 疾病基因数据库 DisGeNET 与 OMIM;③ 转录因子及其对应靶基因数据库 TR

宏基因组学彻底改变了研究人员对微生物群落的认识,微生物组不仅是环境组分,更作为共生体深刻影响着宿主的健康与功能。鉴于微生物群落固有的复杂性及其所处环境的多样性,研究者进行一些宏基因组学研究时必须精心设计以获取能真实反映目标群体特征的准确结果。
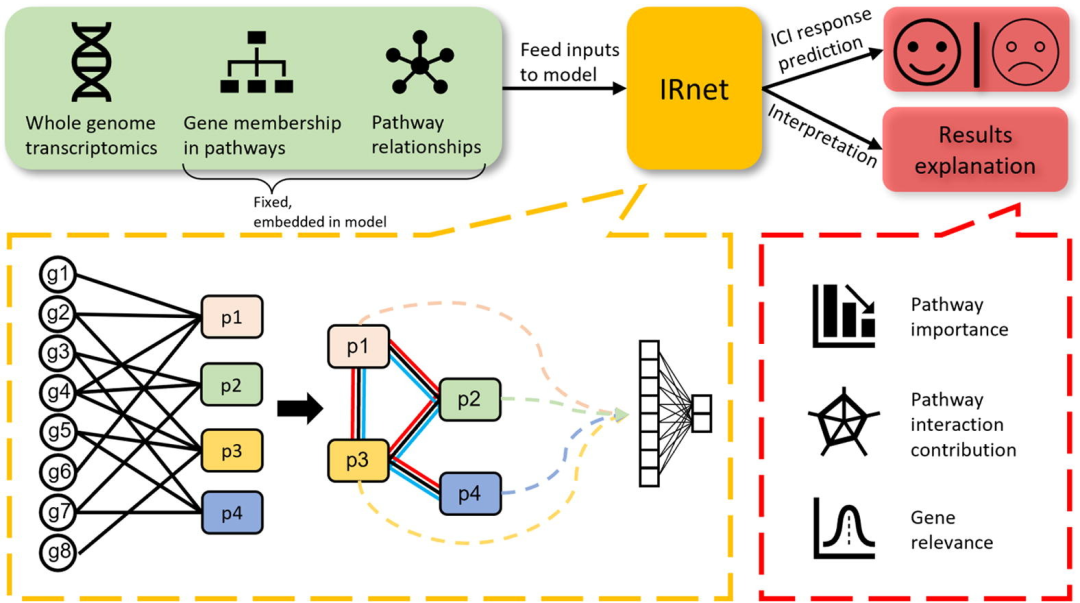
用于预测病人免疫治疗反应类型的生物过程嵌入神经网络,提供通路、通路交互、基因重要性的多重可解释性评估。
每一行代表一个 SNP;每一列代表一个基因,对应填充值为 QTL 结果中 SNP 对基因表达的效应,最后一列为 GWAS 结果中每个 SNP 对所研究性状的效应。此外,还需要。

生信碱移scTenifoldXct,一种结合了细胞内和细胞间基因网络的计算工具,利用 scRNA-seq 数据检测细胞间相互作用。单细胞 RNA 测序(scRNA-seq)能够以稳健且可重复的方式同时收集数万个细胞的转录组信息。利用 scRNA-seq 数据,可以通过复杂组织中细胞特异性配体-受体(LR)的映射来研究细胞通信网络。不断发展的 scRNA-seq 数据空间已经催生了许多用于挖掘细胞间
生信碱移Rtorch经典的统计方法和简单的回归模型在面对复杂的非线性问题时,往往难以有效捕捉数据中的深层次特征。深度学习能够从数据中自动学习特征并进行复杂模式的建模,特别是在图像识别、自然语言处理和基因组学等领域表现卓越。▲ 关于神经网络的易懂讲解,可以点击此处蓝字查看小编的另一篇文章。尽管如此,生信用户最常使用的代码框架是 R 语言,而当前的主流神经网络框架 (如PyTorch) 大多基于 Py

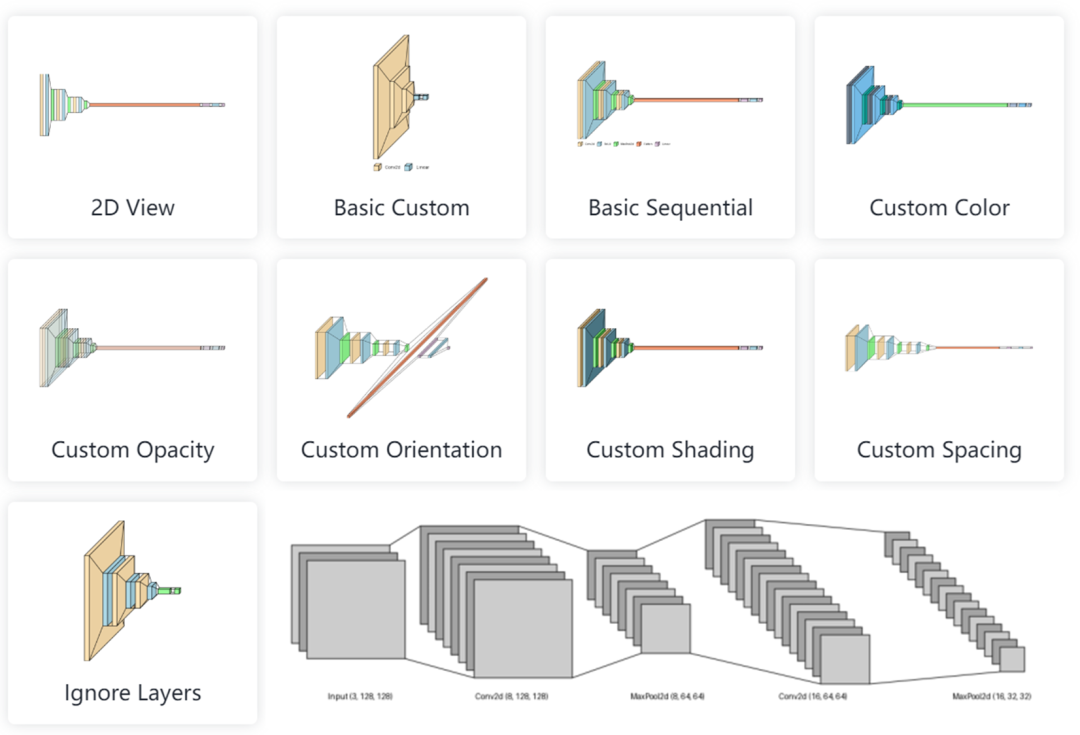
生信碱移torch模块可视化VisualTorch旨在帮助可视化基于Torch的神经网络架构,似乎是今年才上传到github上。它目前支持为PyTorch的Sequential和Custom模型生成分层风格、图形风格和LeNet风格的架构。工具的灵感源自visualkeras、pytorchviz和pytorch-summary。▲ 可视化示例使用以下代码安装该库:环境依赖如下,实测的时候发现py
应对网络上大量不准确的医学图像,NIH BIOART Source 提供经过专业审核的资源,确保图像的高精确性和权威性,助力科学应用与传播。🤩强调一下,该资源暂时还是初始发布(2024年10月7日),后续还会不断扩充图像库,都是支持矢量图片的高质量图片!👥 适用人群: 无论是科研、教学还是医疗领域,NIH BIOART Source 向所有人开放,免费使用,无需注册账号。2. 免费&开放下载: