
简介
该用户还未填写简介
擅长的技术栈
可提供的服务
暂无可提供的服务
训练 ab initio 基因预测工具(以SNAP为例)对于一个新的物种而言,你大概率是没有一个高质量的基因模型去进行基因预测。但是我们可以利用EST序列(少部分物种估计有)、二代测序数据、同源物种蛋白序列,先直接用Maker做基因注释,尽管得到的模型可能不是特别的完美,但可以作为输入反复迭代运行Maker,从而提高最终的表现。这次使用的是下载的练习数据集(见附录)cd ~...
最新登陆服务器的时候,发现我的服务器一直提示,在上一次成功登陆之后,有多少个失败尝试。失败登陆我估计就是有人通过弱口令字典来企图破解我的服务器。之前我对服务器的安全一点都不在乎,而现在我才发现是那么危险。为了杜绝奇奇怪怪的IP地址换着法子来尝试登录你的服务器,我们就需要为我们的云服务器设置一个安全组,首先我们需要点开安全组的实例端口验通实例端口验通...
GeneMarkGeorgia Institute of Technology开发的一系列基因预测工具。真核生物基因组预测主要会用到GeneMark-ES/ET, 其中GeneMark-ES可用于无监督自训练,也就是只要提供一个基因组序列即可,而GeneMark-ET则是在GeneMark-ES的基础上整合了高通量的RNA-Seq转录本数据,工作流程如下工作流程如果...
今天解决解决了一个R包安装的问题,并且硬着头皮把install.packages和download.file的说明从头到位看了一遍,应该再也没有一个R包安装能为难到我了。问题实例问题描述能够用浏览器访问镜像站点,但是在安装R包时遇到如下问题,# CRANWarning in install.packages :unable to access index for r...
Juicer的输出文件: merged_nodups.txtread1的FLAG,对应SAM的第二列,FLAGread1比对的contig,对应SAM的第三列,RNAMEread1比对的contig的位置,对应SAM的第四列,POSread1排序后的位置编号read2的FLAG,对应SAM的第二列,FLAGread2比对的contig,对应SAM的第三列,RNAMEread2比对的...
GeneMarkGeorgia Institute of Technology开发的一系列基因预测工具。真核生物基因组预测主要会用到GeneMark-ES/ET, 其中GeneMark-ES可用于无监督自训练,也就是只要提供一个基因组序列即可,而GeneMark-ET则是在GeneMark-ES的基础上整合了高通量的RNA-Seq转录本数据,工作流程如下工作流程如果...
我用conda创建了R=4.4.3的环境,然后直接用安装,发现会有一堆依赖问题导致无法顺利安装,然后就尝试用conda自己去安装。我先用了默认的conda包管理工具结果是一堆冲突,简单就说,我在当前的R=4.4.3环境下办不到。那我试试mamba呢?毕竟mamba可比conda快多了这下不报错了,但是我定睛一看,他这是要改我的R的环境啊!这肯定不能同意。那咋办呢?那就只能老老实实,自己解决依赖问题

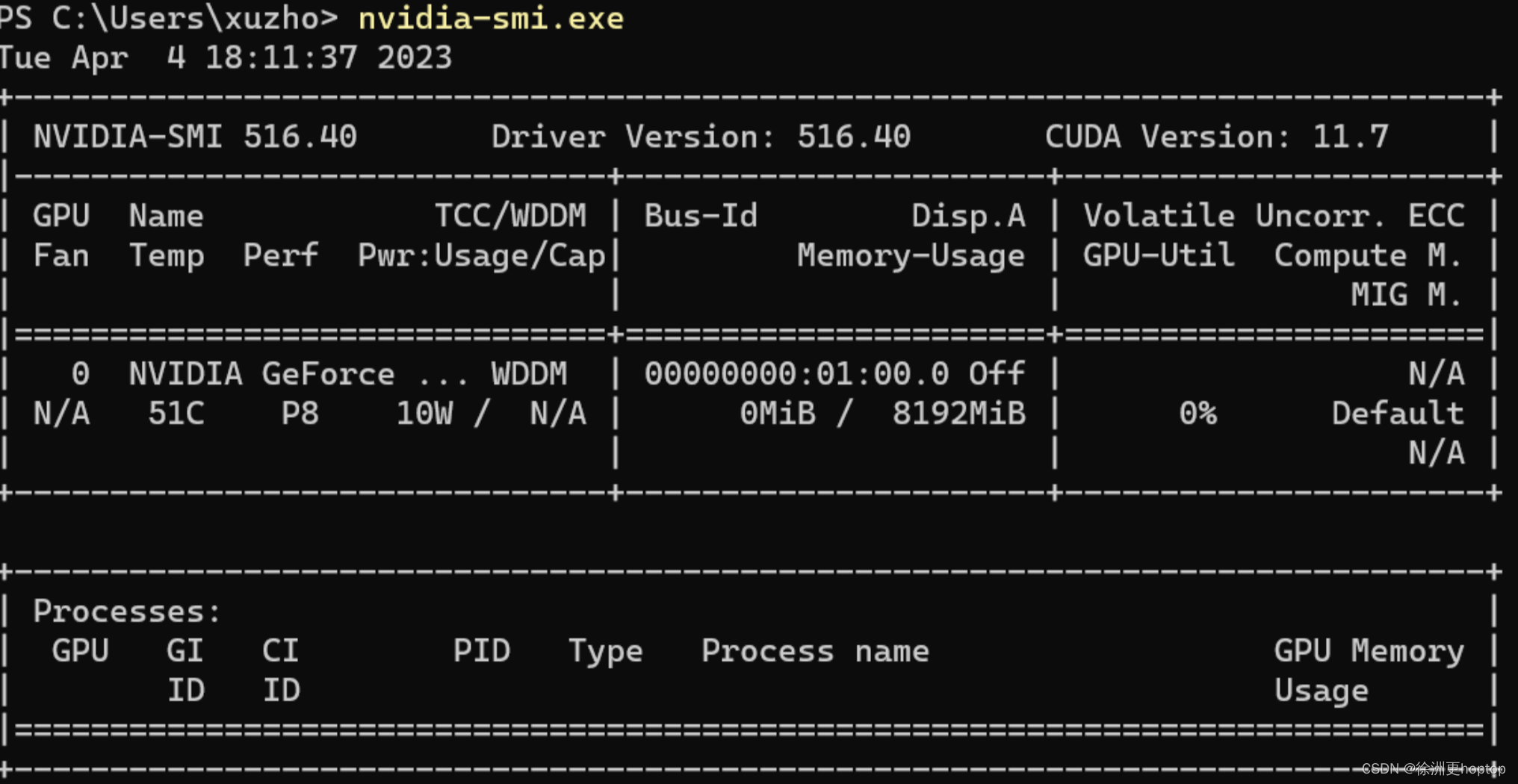
Pytorch是目前最火的深度学习框架之一,另一个是TensorFlow。不过我之前一直用到是CPU版本,几个月前买了一台3070Ti的笔记本(是的,我在40系显卡出来的时候,买了30系,这确实一言难尽),同时我也有一台M1芯片Macbook Pro,目前也支持了pytorch的GPU加速,所以我就想着,在这两个电脑上装个Pytorch,浅度学习深度学习。
三代数据由于其高错误率(目前应该是10%左右), 即便在组装前有一步纠错环节,但是组装得到序列依旧存在着许多错误,因此需要进行polish环节。polish分为两个层次,三代原始序列polish和二代序列polish。其中三代纠错这一步速度会很慢,所以有些人会选择直接用二代序列进行纠错。(从我个人项目经验来看,直接用二代纠错的效果和先三代再二代区别并没有那么显著,也有可能是我的项目...
首先访问SRA的提交界面,https://submit.ncbi.nlm.nih.gov/subs/sra/,在没有登陆NCBI时,网页内容如下所示未登录时点击Log in, 会进入一个新的网页用于登陆或者创建新的NCBI账户。登陆NCBI在创建完账号或者登陆之后,返回之前的SRA上传页面,界面就变成了如下。登陆后他提示了有三种方法可...










