
简介
该用户还未填写简介
擅长的技术栈
可提供的服务
暂无可提供的服务
Amber26 与 AmberTools26 是 Amber 分子动力学模拟生态的重要更新。AmberTools26 强化了 conda 安装、体系准备、小分子参数化、PBSA GPU 后端、cpptraj 分析和 RNA / pGM 力场相关能力;Amber26 则通过 pmemd、pmemd.cuda、炼金术自由能计算、LIG-GaMD、REMD reservoir 和 GBION 等功能,进

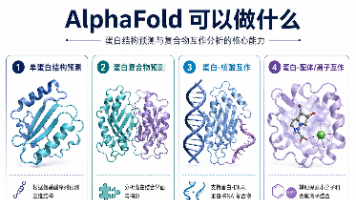
AlphaFold3标志着AI蛋白质预测技术从单蛋白结构迈向分子互作分析的新时代。与AlphaFold2相比,其核心突破在于能够预测蛋白复合物、蛋白-核酸、蛋白-配体等相互作用体系,为生物分子互作研究提供全新工具。该系统可生成互作界面分析、接触概率、结构可信度(pLDDT/PAE/ipTM)等关键指标,适用于蛋白互作、核酸识别、药物设计等研究场景。但需注意预测结果需结合多维度评估指标,不能替代实验
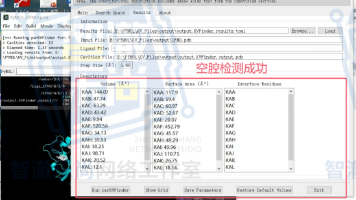
PyMOL 作为蛋白质结构分析工具的价值远超基础可视化功能,其插件生态能显著提升酶催化与蛋白结构研究的工作效率。本文重点介绍了 5 款实用插件:PyMOL Optimize(分子结构预处理)、PyMOL GetBox(对接区域获取)、CAVER(酶通道分析)、ParKVFinder-win(蛋白空腔检测)和 PyVOL(口袋可视化),它们共同构成了从结构观察到结果表达的完整分析链条。这些插件虽安装
yMolAI 是一款构建在开源 PyMOL 基础上的 AI 助手插件,它将自然语言交互、分子结构可视化与结构分析工作流结合在一起,让研究者能够以更直观的方式完成蛋白质结构观察、活性位点展示、配体结合模式分析以及科研图片整理等任务。对于从事酶催化、蛋白结构、生物信息、分子对接和蛋白工程方向的研究生与博士来说,PyMolAI 的价值不仅体现在“更智能”,更体现在“更高效”。它降低了 PyMOL 的使用
本文针对Mac电脑(M系列芯片)安装Schrodinger软件的特殊需求,提供了一套完整的安装方案。目前该软件在macOS平台安装面临三大难点:M芯片架构特殊、官方文档稀缺、依赖环境复杂。文章详细解析了从获取DMG安装文件、配置环境变量到License授权的全流程,并验证了Maestro、Glide、Desmond等核心模块的可用性。相比于Windows系统,macOS安装虽然存在技术门槛,但在命
在分子动力学模拟中,MM/PBSA(分子力学-泊松-玻尔兹曼表面积)和 MM/GBSA(分子力学-广义玻恩表面积)方法被广泛用于估算生物分子复合物的结合自由能。针对 GROMACS 生成的轨迹文件,主要有两种工具可用于执行这些计算:gmx_mmpbsa.sh 和 gmx_MMPBSA。本文将详细比较这两者的特点、适用场景及各自优势,以帮助大家选择最适合的工具。











