pfam基本介绍,以及蛋白质序列下载
Pfam网站地址:http://pfam.xfam.org/主页面1. 检索序列搜索:分析您的蛋白质序列以进行Pfam匹配查看PFAM条目:查看Pfam批注和对齐方式查看一个clan:查看相关条目组查看序列:查看蛋白质序列的结构域组织查看结构:在PDB结构上查找域关键词搜索:通过PFAM号检索:2. 浏览其中一些关键词:Domain: 一个结构单元 Motif: A short unit foun
·
Pfam网站地址:http://pfam.xfam.org/
主页面
1. 检索

- 序列搜索:分析您的蛋白质序列以进行Pfam匹配
- 查看PFAM条目:查看Pfam批注和对齐方式
- 查看一个clan:查看相关条目组
- 查看序列:查看蛋白质序列的结构域组织
- 查看结构:在PDB结构上查找域
- 关键词搜索:
- 通过PFAM号检索:
2. 浏览

其中一些关键词:
Domain: 一个结构单元 Motif: A short unit found outside globular domains
CLAN: 对多个family进行相似性分析,将具有相似的三维结构或者相同motif的family归为一个clan,
可以看做是superfamily的概念,每个clan以CL编号标识。
proteones:物种的蛋白质组信息,就是该物种内所有的蛋白质family 信息
3. 家族选择
上图中选择了“top twenty”,出现的是序列数量前20的家族(family)
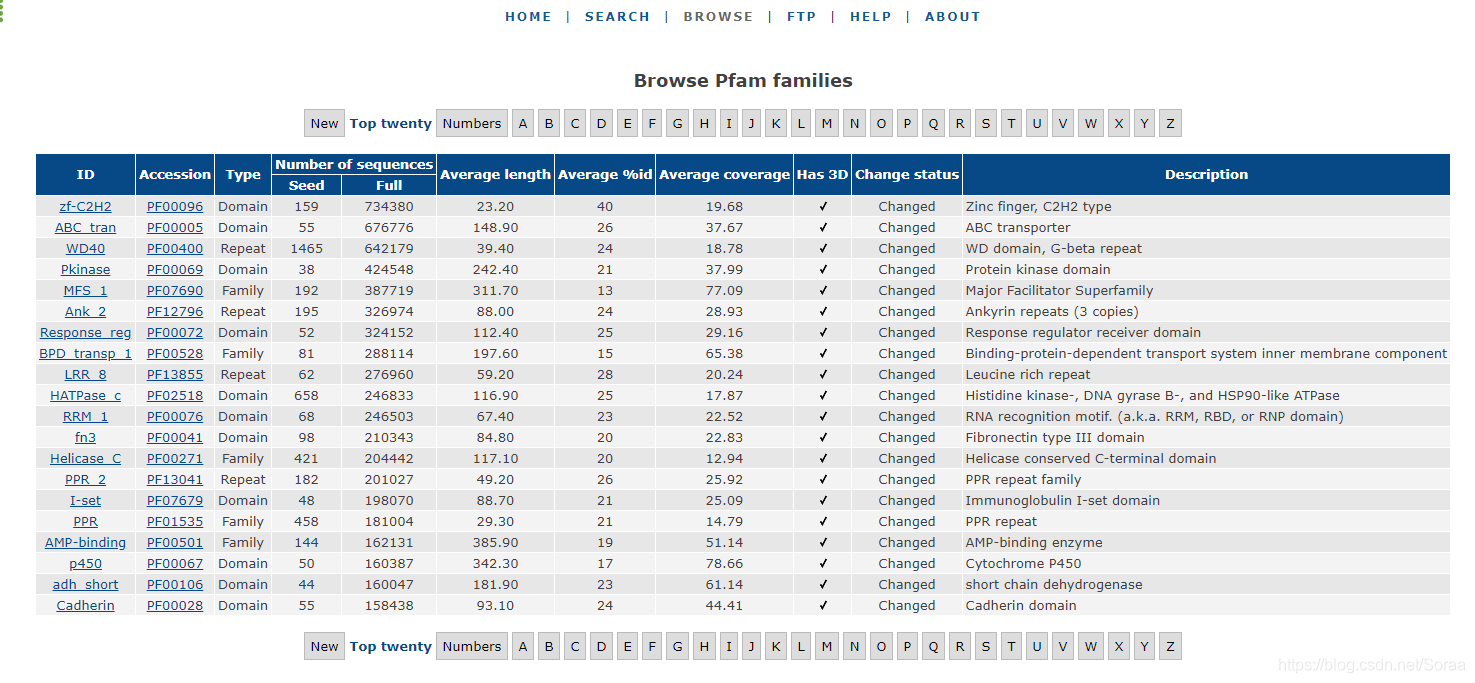
- ID:家族id
- Accession:PF号,每个家族稳定的唯一标志
- 家族类型:分为Domain,Family,Repeat,Motifs,Coiled-Coil,Disordered
- 序列数量:seed:number of regions in the seed alignment.
full: number of regions in the full alignment - 平均长度:完全比对后氨基酸区域的平均长度
- 平均%id:Average percentage identity of sequences in the full alignment
- 平均覆盖率:pfam条目覆盖整个序列长度的分数 fraction of whole sequence length that pfam entry covers
- 有无3d:
- 修改状态:与上个版本是否有改变
- 描述
5. 家族介绍
随便点开一个蛋白质家族是这样一个场景
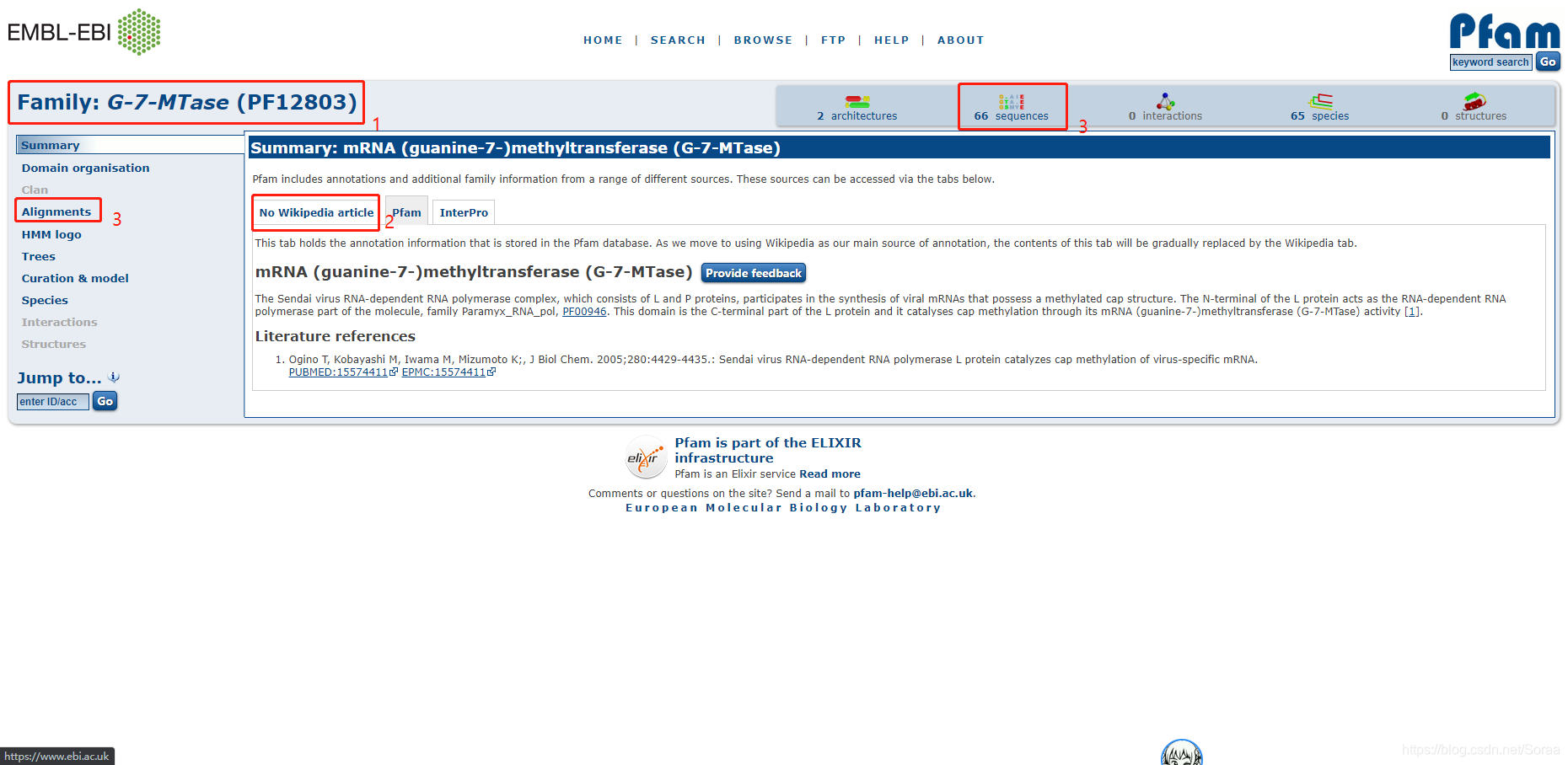
- 为家族名称以及家族的PF号
- 是该家族在维基百科中的介绍页面
- 是两处,点击之后出现的是相同的页面,即比对序列及下载。
5. 序列下载
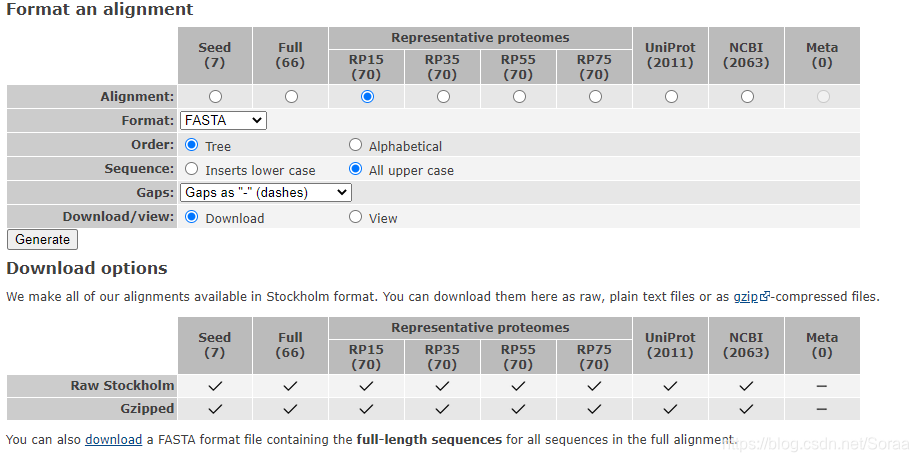
1. format an alignment:
1.1 Alignment: 选择算法
1.2 Format: 选择文件格式:这里选择fasta文件
1.3 Order: 选择顺序,alphabetical是按蛋白质序列首字母顺序排序的。
1.4 Sequence: 全大写字母,或是插入小写(不知道意义)
1.5 Gaps:对齐序列插入 可以选择“-”,“.”或者mix两者都有或者不插入
1.6 Download/view: 选择下载还是视图中查看
其中,有些家族过大是没法进行序列比对的,所以在Alignment上会有一些地方不能勾选。
2. Download
下载未比对过的全长度fasta格式的文件,并用.gzip打包。
更多推荐
 已为社区贡献1条内容
已为社区贡献1条内容








所有评论(0)